兄弟姐妹们好,我在学校参加了个比赛,大概是在TCGA网上下载一份癌症的数据(我下的是TCGA-UCEC)然后用R语言进行数据预处理之后继续用R语言绘制图片例如pca图跟火山图之类的,但我只知道这两个,老湿说把数据分析完绘制图形后要写论文,我不知道还要绘制哪些图,可不可以分享一些思路或经验😭
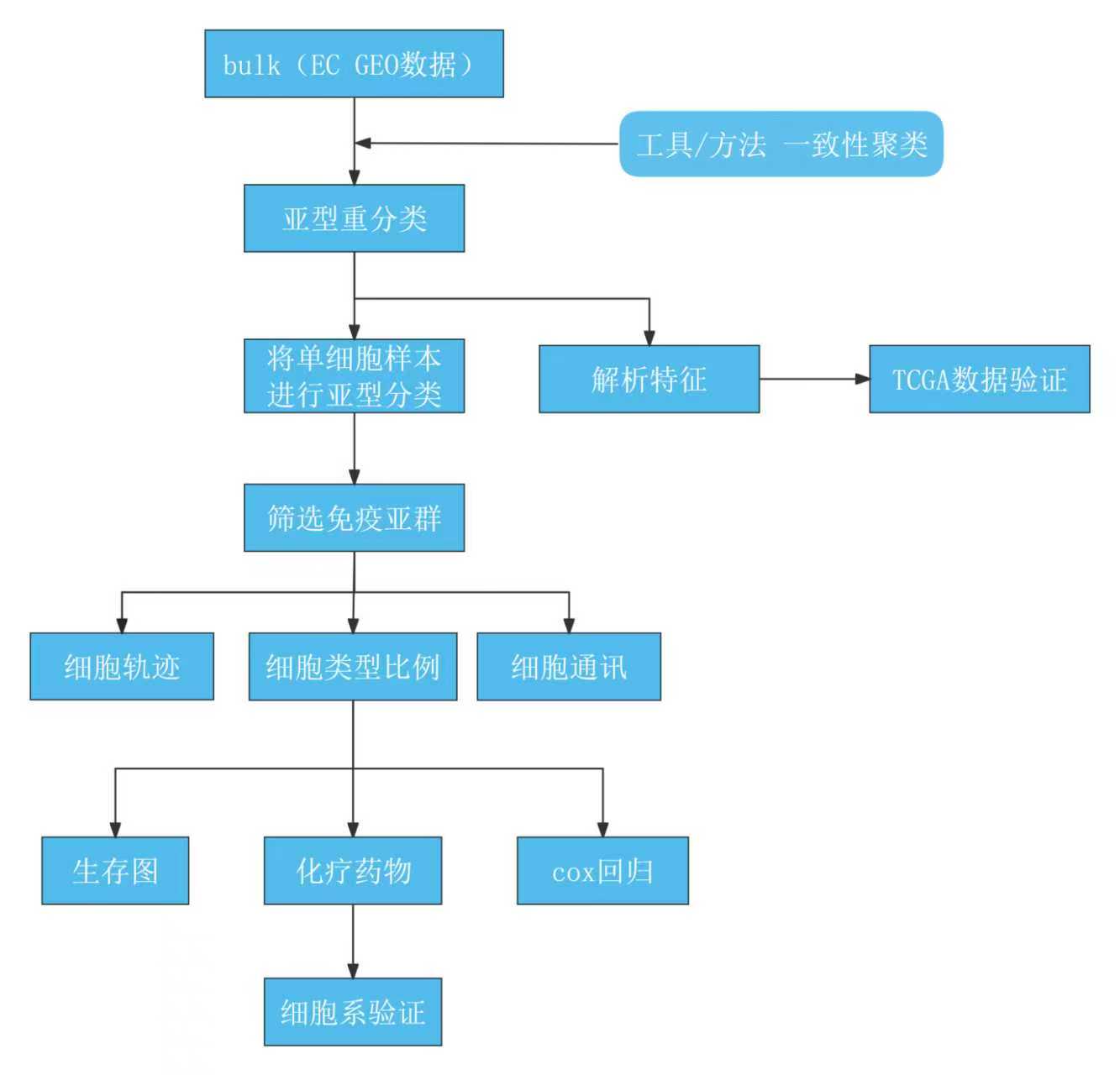
图是老湿给的大概流程图
兄弟姐妹们好,我在学校参加了个比赛,大概是在TCGA网上下载一份癌症的数据(我下的是TCGA-UCEC)然后用R语言进行数据预处理之后继续用R语言绘制图片例如pca图跟火山图之类的,但我只知道这两个,老湿说把数据分析完绘制图形后要写论文,我不知道还要绘制哪些图,可不可以分享一些思路或经验😭

上午好☀️☀️☀️️
本答案参考通义千问
在进行癌症数据(如TCGA-UCEC)的预处理后,绘制合适的图形对于数据分析和论文撰写非常重要。这些图形可以帮助你更直观地理解数据特征、差异表达基因、样本分组、通路富集等信息。以下是一些必须绘制或推荐绘制的图形,并附上详细说明与示例代码。
library(ggplot2)
library(pcaMethods)
# 假设你的数据是表达矩阵,行是基因,列是样本
pca_result <- pca(data_matrix, ncomp = 3)
scores <- as.data.frame(pca_result$scores)
# 绘制3D PCA图
ggplot(scores, aes(x = PC1, y = PC2, color = group)) +
geom_point(size = 3) +
labs(title = "PCA Plot", x = "PC1", y = "PC2")
library(ggplot2)
# 假设你有差异分析结果 df,包含 log2FC 和 p.value 列
df$significant <- ifelse(abs(df$log2FC) > 1 & df$p.value < 0.05, "Significant", "Not Significant")
ggplot(df, aes(x = log2FC, y = -log10(p.value), color = significant)) +
geom_point() +
theme_minimal() +
labs(title = "Volcano Plot", x = "log2(Fold Change)", y = "-log10(P-value)")
library(ggplot2)
library(pheatmap)
# 假设 data_matrix 是表达矩阵
pheatmap(data_matrix,
scale = "row",
clustering_distance_rows = "euclidean",
clustering_method = "complete",
color = colorRampPalette(c("blue", "white", "red"))(50))
library(ggplot2)
# 假设 df 包含样本类型(group)和表达值(expression)
ggplot(df, aes(x = group, y = expression, fill = group)) +
geom_boxplot() +
theme_minimal() +
labs(title = "Expression Distribution by Group", x = "Group", y = "Expression")
library(ggplot2)
library(reshape2)
# 计算样本间的相关性
cor_matrix <- cor(data_matrix)
cor_df <- melt(cor_matrix)
ggplot(cor_df, aes(x = Var1, y = Var2, fill = value)) +
geom_tile() +
scale_fill_gradient2(low = "blue", mid = "white", high = "red") +
theme_minimal() +
labs(title = "Sample Correlation Matrix")
enrichplot包绘制条形图或气泡图。library(enrichplot)
# 假设你已经进行了富集分析,得到一个 enrich_result 对象
barplot(enrich_result, showCategory = 10)
survival 和 survminer 包。library(survival)
library(survminer)
# 假设你有 survival_data 包含 time 和 status 列
fit <- survfit(Surv(time, status) ~ group, data = survival_data)
ggsurvplot(fit, data = survival_data, risk.table = TRUE)
library(ggplot2)
# 假设 gene_expression 是某基因的表达值
ggplot(data = data.frame(sample = rownames(gene_expression), value = gene_expression),
aes(x = sample, y = value, group = 1)) +
geom_line() +
geom_point() +
theme_minimal() +
labs(title = "Gene Expression Trend", x = "Sample", y = "Expression")
如果你需要进一步帮助,比如如何从TCGA下载数据、如何用R做差异分析或富集分析,我也可以继续为你提供详细指导!💪