晚上好🌙🌙🌙
本答案参考通义千问
你遇到的 FoldX 5.1 使用问题非常具有代表性,尤其是在进行 单点饱和突变(Single Point Saturation Mutagenesis, SPSM) 和 ΔΔG 计算 时。以下是对你的问题的详细分析与解决方案。
一、问题分析
1. BuildModel 命令无法识别残基
你提到使用 PositionScan 报错 Specified residue not found,即使指定了 --positions=210,说明 FoldX 未能正确解析 PDB 文件中的残基信息。
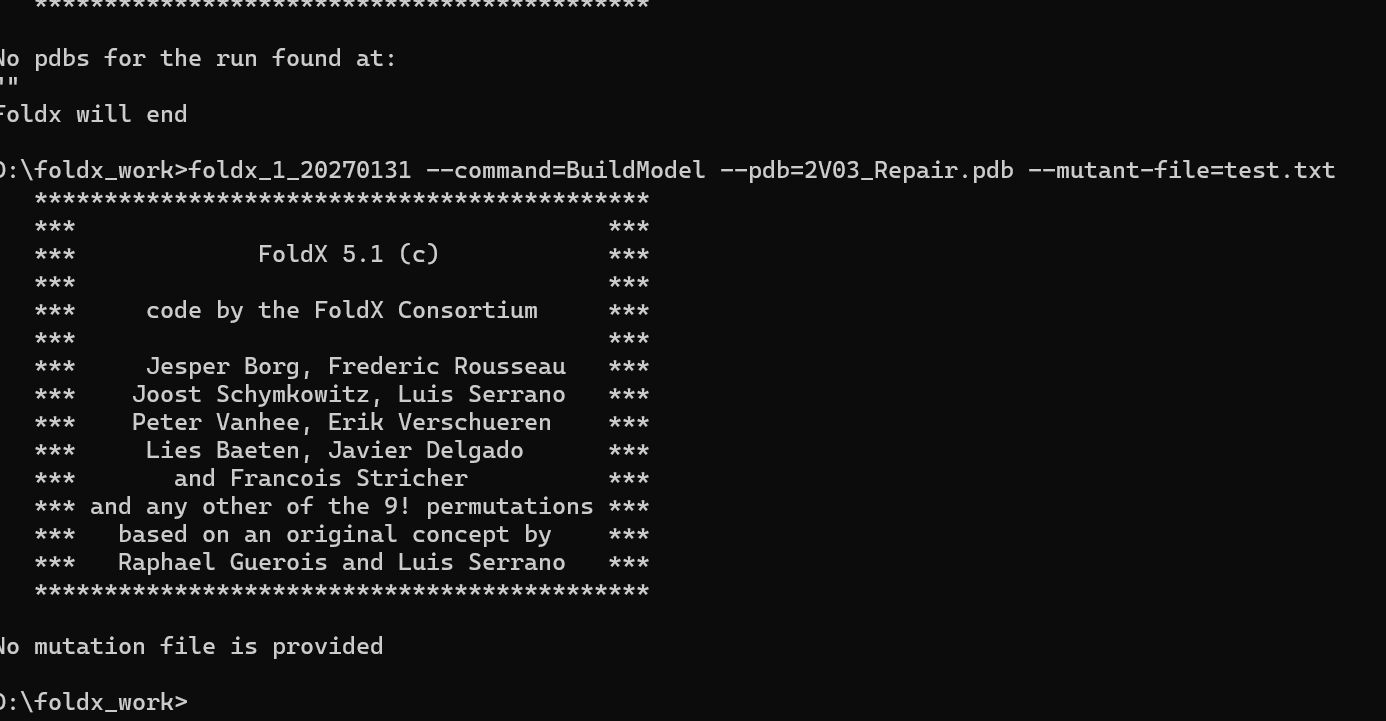
2. BuildModel 提示 No mutation file is provided
尽管文件路径和名称正确,但 FoldX 仍报错,说明可能不是文件路径问题,而是 格式或内容不符合要求。
3. 尝试过的突变文件格式无效
你尝试了多种格式,如 A210A, ARG210ALA, ARG210, A ALA R210A 等,但均失败,表明 突变文件格式不被 FoldX 支持。
4. PDB 文件修复后依然存在问题
虽然你已经运行了 RepairPDB 并生成了 _Repair.pdb,但 FoldX 仍然无法识别残基,可能是 链标识符、原子顺序、或残基编号格式问题。
二、解决方案
✅ 重点解决步骤:
1. 确保 PDB 文件格式符合 FoldX 要求
- 链标识符必须为大写(例如
A 而非 a)。 - 残基编号必须是整数,不能包含空格或其他字符。
- 每个残基必须有完整的原子信息(如 Cα、Cβ 等)。
- 避免使用稀有氨基酸或非标准残基。
建议: 使用 pdbtools 或 Biopython 检查并清理 PDB 文件。
2. 正确构建突变文件格式
FoldX 的突变文件需要是 每行一个突变,格式如下:
<Residue><Chain><Position><Mutation>
例如:
ARGA210ALA
ARGA210GLY
...
注意:
- 链标识符必须是大写。
- 残基名首字母必须是大写。
- 位置号必须是整数。
- 请勿在突变文件中添加额外空格或注释。
3. 使用正确的 BuildModel 命令
foldx_1_20270131 --command=BuildModel \
--pdb=2V03_Repair.pdb \
--mutant-file=mutant_list.txt \
--output=mutant_model.pdb
关键点:
--mutant-file 必须是文本文件,且每行是一个突变。- 确保
mutant_list.txt 与执行命令的目录一致。
4. 使用 PositionScan 进行 ΔΔG 计算
foldx_1_20270131 --command=PositionScan \
--pdb=2V03_Repair.pdb \
--positions=210,211,212,213,214,215,216 \
--output=position_scan_result.txt
注意: --positions 参数支持逗号分隔的多个位置。
三、代码示例(修改后的突变文件)
假设你要对 7 个残基(210~216)进行单点饱和突变,可以创建如下 mutant_list.txt:
ARGA210ALA
ARGA210ARG
ARGA210GLY
ARGA210LEU
ARGA210VAL
ARGA210ILE
ARGA210MET
...
(重复以上模式,针对 211~216)
注意: 你可以用 Python 自动生成这个文件,例如:
import itertools
residues = ['ALA', 'ARG', 'GLY', 'LEU', 'VAL', 'ILE', 'MET']
positions = [210, 211, 212, 213, 214, 215, 216]
with open('mutant_list.txt', 'w') as f:
for pos in positions:
for res in residues:
line = f"ARGA{pos}{res}\n"
f.write(line)
四、替代方案
如果你发现 FoldX 5.1 实在难以适配,可以考虑以下替代方案:
1. PyRosetta(推荐)
2. FreeDDG(免费在线工具)
- 可以上传 PDB 文件,自动计算 ΔΔG。
- 支持多点突变。
- 网站:http://ddg.biocomp.ucdavis.edu/
3. Rosetta@Home(分布式计算)
- 用于大规模蛋白质结构预测和稳定性分析。
- 需要安装客户端,适合高通量任务。
五、总结
| 问题 | 解决方法 |
|------|----------|
| Specified residue not found | 确保 PDB 中残基编号为整数,链标识符为大写 |
| No mutation file is provided | 确保突变文件格式正确,每行一个突变 |
| 突变文件格式错误 | 使用 ARGA210ALA 格式,不要用其他格式 |
| PDB 修复后仍出错 | 使用 pdbtools 或 Biopython 检查 PDB 格式 |
| 无法批量处理 | 使用 Python 自动生成突变列表 |
六、附录:FoldX 5.1 常见错误排查表
| 错误信息 | 原因 | 解决方法 |
|----------|------|----------|
| Specified residue not found | PDB 中无该残基或编号不对 | 检查 PDB 文件,确保残基存在 |
| No mutation file is provided | 突变文件格式或路径错误 | 检查文件路径和格式 |
| Invalid mutant format | 突变文件格式错误 | 使用 ARGA210ALA 格式 |
| Invalid chain identifier | 链标识符为小写 | 修改为大写(如 A) |
如果你还有其他具体错误信息或日志内容,欢迎提供,我可以进一步帮你定位问题。希望这些信息能帮助你顺利完成 ΔΔG 计算!🙏