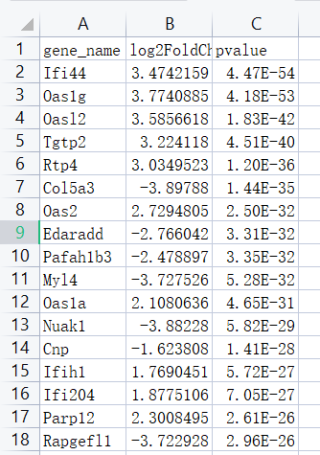
问题,绘制火山图时使用case when函数报错,读入文件格式如图,代码如下。请问报错原因是什么?是否是因为R语言并非最新版或是数据格式有误,数据仅包含gene name、log2FC、pvalue三列。如果需要补充信息请留意
> library(EnhancedVolcano)
> library(tidyverse)
── Attaching core tidyverse packages ────────────────────────────────────────── tidyverse 2.0.0 ──
✔ dplyr 1.1.1 ✔ readr 2.1.4
✔ forcats 1.0.0 ✔ stringr 1.5.0
✔ lubridate 1.9.2 ✔ tibble 3.2.1
✔ purrr 1.0.1 ✔ tidyr 1.3.0
── Conflicts ──────────────────────────────────────────────────────────── tidyverse_conflicts() ──
✖ dplyr::filter() masks stats::filter()
✖ dplyr::lag() masks stats::lag()
ℹ Use the conflicted package to force all conflicts to become errors
Warning messages:
1: 程辑包‘tidyverse’是用R版本4.2.3 来建造的
2: 程辑包‘tibble’是用R版本4.2.3 来建造的
3: 程辑包‘tidyr’是用R版本4.2.3 来建造的
4: 程辑包‘readr’是用R版本4.2.3 来建造的
5: 程辑包‘purrr’是用R版本4.2.3 来建造的
6: 程辑包‘dplyr’是用R版本4.2.3 来建造的
7: 程辑包‘forcats’是用R版本4.2.3 来建造的
8: 程辑包‘lubridate’是用R版本4.2.3 来建造的
> df <- read.csv("volcano.csv", header = T,row.names = 1)
>group<-case_when(df$log2FoldChangeC<(-1)&df$pvalue<0.05 ~"#9AAFEF",
+ df$log2FoldChange>(1)&df$pvalue<0.05 ~"#EDB4B4",
+ df$pvalue >= 0.05 ~"#b5b5b5",
+ abs(df$log2FoldChange)<= 1 ~"#b5b5b5")
Error in `case_when()`:
! Can't recycle `..1 (left)` (size 0) to match `..2 (left)` (size 1271).
Run `rlang::last_trace()` to see where the error occurred.