晚上好🌙🌙🌙
本答案参考通义千问
你遇到的问题是关于 Monocle2 在使用 newCellDataSet 函数创建 CellDataSet 对象(即 mycds)后,在运行 upgrade_graph(mycds) 时出现错误,并且 mycds 的内容几乎为空。这是一个比较常见的问题,尤其是在 Monocle2 中,如果数据结构没有正确构建,或者依赖的 igraph 包版本不兼容,就容易出现这种错误。
✅ 问题分析
1. 报错信息
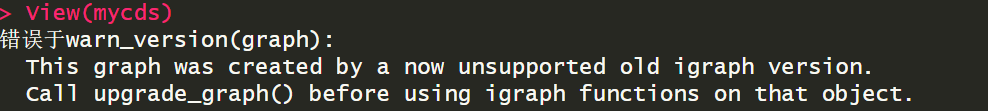
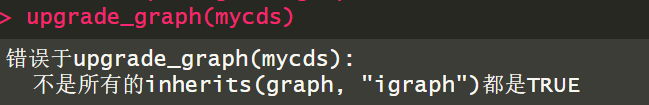
错误于upgrade_graph(mycds): 不是所有的inherits(graph, "igraph")都是TRUE
这说明 mycds 中的图结构(graph)不是 igraph 类型的对象,也就是说:
mycds 没有正确初始化;- 或者
newCellDataSet 没有正确构造图结构; - 或者
igraph 版本与 Monocle2 不兼容。
2. Global Environment 中 mycds 是空的
这表明:
mycds 可能没有被正确生成;- 或者
newCellDataSet 的参数设置不正确; - 或者你的数据格式不符合 Monocle2 的要求。
🔧 解决方案
以下是逐步排查和解决该问题的方法,请按照顺序执行:
1. 检查数据格式是否符合 Monocle2 要求
Monocle2 需要一个 基因表达矩阵,其行是基因,列是细胞,并且每个单元格是一个数值(如 TPM、FPKM、counts 等)。
示例:
# 假设你的数据存储在 data_matrix 中
dim(data_matrix) # 应为 (n_genes, n_cells)
# 查看前几行
head(data_matrix)
如果数据格式不对,请先进行预处理(如转置、标准化等)。
2. 确保正确安装并加载所有依赖包
Monocle2 依赖以下包:
monocleigraphggplot2BiocManager
请确保这些包都已安装并更新到兼容版本。
# 安装或更新 monocle
if (!requireNamespace("BiocManager", quietly = TRUE))
install.packages("BiocManager")
BiocManager::install("monocle")
# 安装或更新 igraph
install.packages("igraph")
# 加载包
library(monocle)
library(igraph)
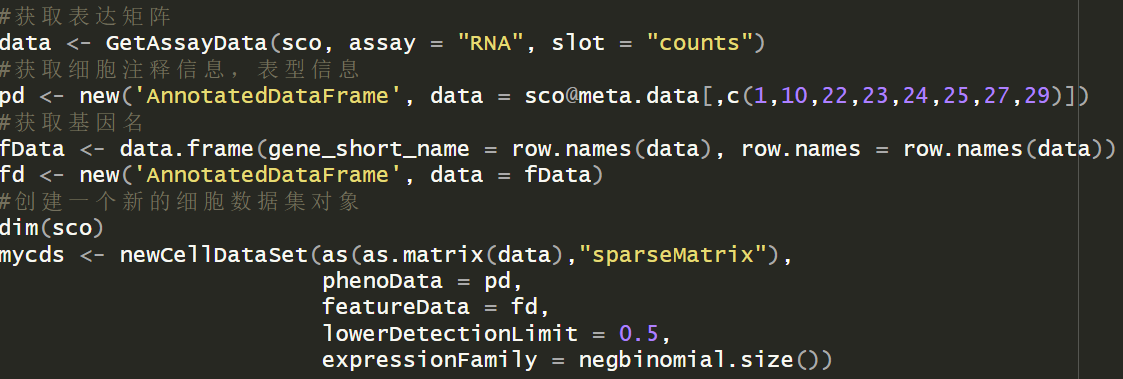
3. 使用正确的 newCellDataSet 参数
Monocle2 的 newCellDataSet 函数需要以下参数:
expression_data:基因表达矩阵cell_metadata:细胞元数据(可选)gene_metadata:基因元数据(可选)
示例代码:
# 假设 data_matrix 是你的基因表达矩阵
# cell_info 是包含细胞元数据的数据框(如批次、条件等)
mycds <- newCellDataSet(
expression_data = data_matrix,
cell_metadata = cell_info,
gene_metadata = NULL,
lower_detection_limit = 0.5
)
注意: 如果你没有提供 cell_metadata,可以留空(NULL),但必须确保 expression_data 是一个完整的矩阵。
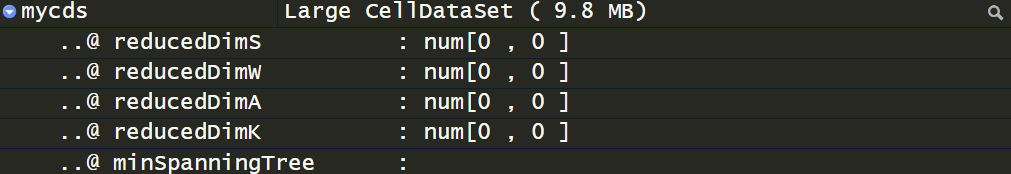
4. 检查 mycds 是否成功创建
在 R 控制台中运行:
str(mycds)
你应该看到类似如下输出(部分字段):
Formal class 'CellDataSet' [package "monocle"] with 6 slots
..@ expression: num [1:1000, 1:50] 1.2 3.4 0.5 ...
..@ cellData : data frame with 50 rows and 1 column
..@ geneData : data frame with 1000 rows and 1 column
..@ graph : list()
..@ model : list()
..@ ... : ...
如果 graph 字段为空(list()),说明图结构未被初始化。
5. 手动初始化图结构(如果需要)
如果 graph 字段为空,你可以尝试手动构建图结构(例如基于 UMAP 或 PCA 的降维结果)。
# 使用 UMAP 进行降维
mycds <- reduceDimension(mycds, method = "UMAP")
# 构建图结构
mycds <- buildGraph(mycds)
然后再次尝试:
mycds <- upgrade_graph(mycds)
6. 检查 igraph 版本兼容性
Monocle2 通常兼容 igraph 1.x 或 2.x,但某些版本可能存在兼容性问题。
建议版本:
igraph 1.2.10(推荐)igraph 2.1.0(可能可行,但需测试)
你可以尝试降级或升级 igraph:
# 卸载当前 igraph
remove.packages("igraph")
# 安装指定版本(如 1.2.10)
install.packages("https://cran.r-project.org/src/contrib/Archive/igraph/igraph_1.2.10.tar.gz", repos = NULL, type = "source")
注意:安装源码版需要编译环境,建议使用 CRAN 提供的二进制包。
7. 检查 R 和 Monocle2 的版本兼容性
你目前使用的是:
- R 4.5.1(较新)
- monocle 2.36.0
- igraph 2.1.4
建议:
- 升级
monocle 到最新版本(如 2.38.0 或更高); - 或者降级
igraph 到 1.2.10; - 或者使用 R 4.4.0 以避免潜在的兼容性问题。
🧠 总结解决方案(有序列表)
- 检查数据格式是否符合 Monocle2 要求,确保
expression_data 是一个完整的基因表达矩阵。 - 安装并加载所有依赖包,包括
monocle、igraph、BiocManager 等。 - 使用正确的
newCellDataSet 参数,确保 expression_data 正确传入。 - 检查
mycds 是否成功创建,查看 str(mycds) 输出中的 graph 字段是否为空。 - 手动构建图结构,使用
reduceDimension 和 buildGraph 初始化图。 - 检查
igraph 版本兼容性,建议使用 igraph 1.2.10。 - 考虑 R 和 Monocle2 的版本兼容性,必要时升级或降级版本。
💡 补充建议
如果你能提供以下信息,我可以进一步帮助你调试:
str(data_matrix) 的输出;str(cell_info) 的输出;- 完整的
newCellDataSet 调用代码; - 报错的完整日志(截图或文本)。
如有更多问题,欢迎继续提问!