在跑单细胞时碰到这个cluster(图中的cluster29)nCount_RNA和nFeature_RNA和别的cluster都不一样,并且在umap图中位置比较偏,细胞数也少,请问这个是由于doublets未去除干净导致的吗?这个cluster可以删除吗
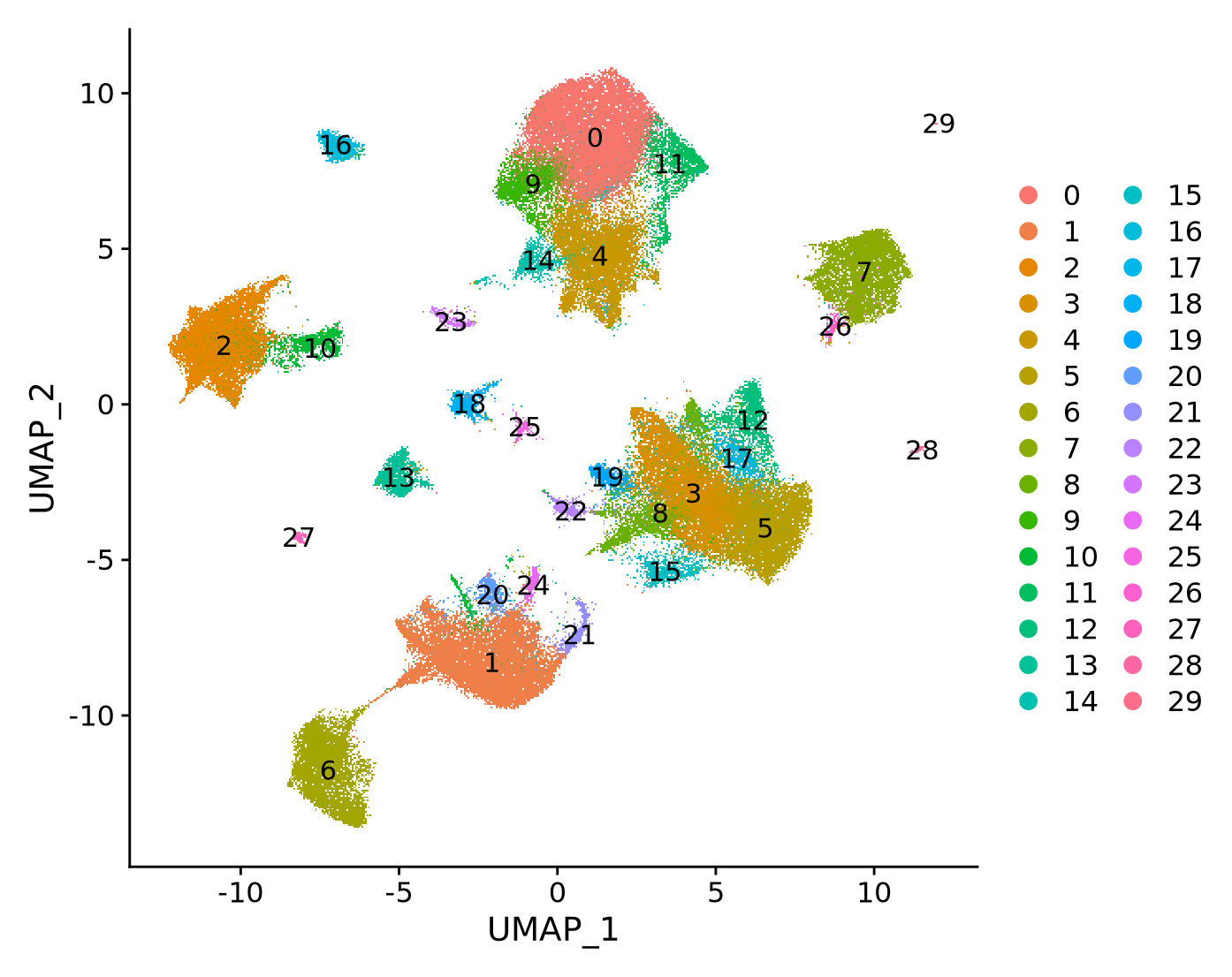
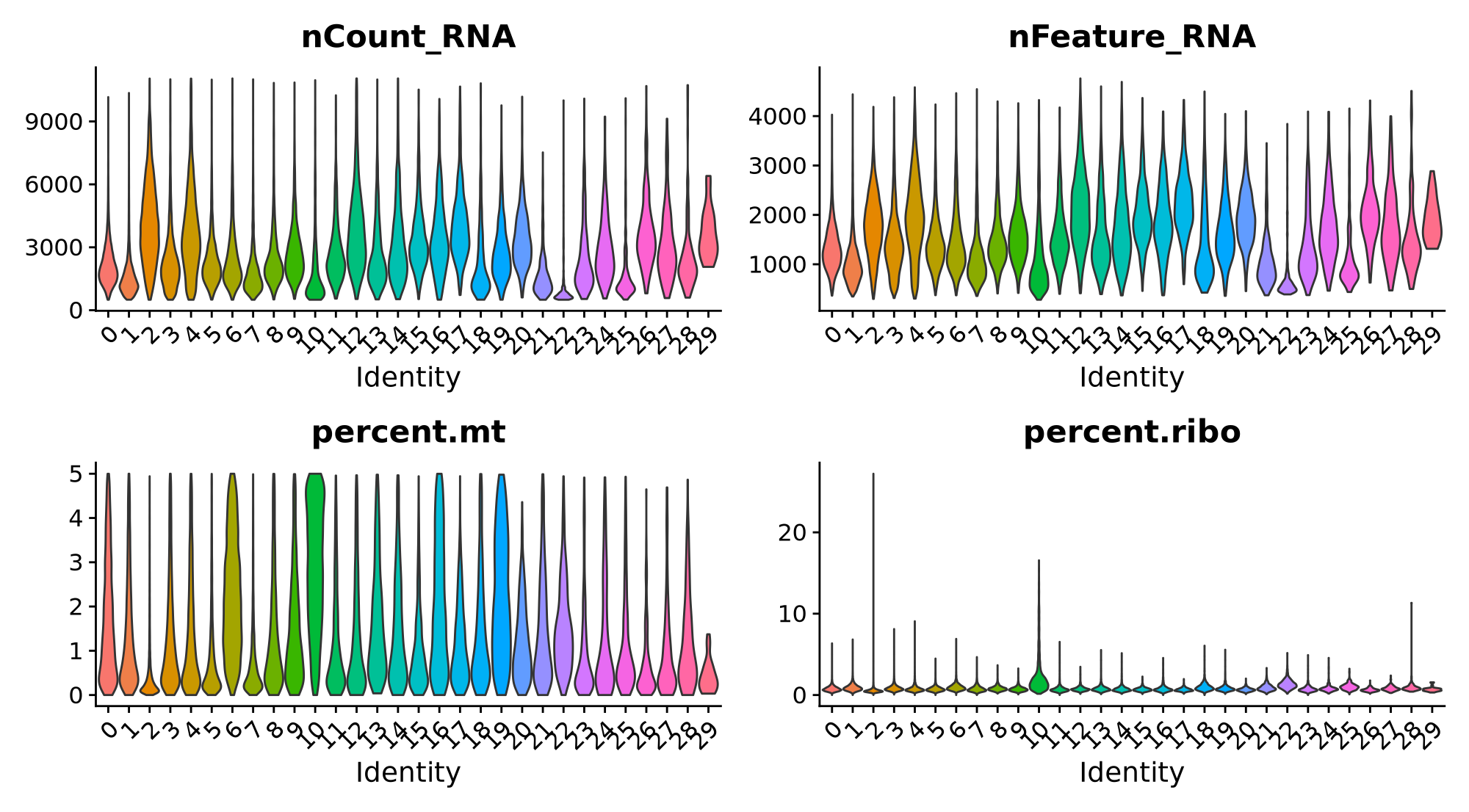
在跑单细胞时碰到这个cluster(图中的cluster29)nCount_RNA和nFeature_RNA和别的cluster都不一样,并且在umap图中位置比较偏,细胞数也少,请问这个是由于doublets未去除干净导致的吗?这个cluster可以删除吗


下午好🌅🌅🌅
本答案参考通义千问
在单细胞分析中,遇到一个与其它cluster差异显著、位置偏移、细胞数量少的cluster(如你提到的cluster29),确实需要仔细评估其是否为双细胞(doublets)或异常细胞。以下是详细的分析和解决方案:
nCount_RNA 和 nFeature_RNA 显著不同
UMAP位置偏移
细胞数量少
可以删除,但需谨慎操作,并确保不影响整体分析结果。
doubletScores 或 scDblFinder 检测双细胞# 使用 scDblFinder 检测双细胞
library(scDblFinder)
dblf <- scDblFinder(seu, use.dimred = "UMAP")
plot(dblf)
# 查看哪些细胞被标记为双细胞
seu@meta.data$doublet <- dblf$doublet
nCount_RNA 和 nFeature_RNA 分布# 绘制每个cluster的nCount_RNA分布
plot_data <- as.data.frame(seu@meta.data)
plot_data$nCount_RNA <- as.numeric(plot_data$nCount_RNA)
ggplot(plot_data, aes(x = cluster, y = nCount_RNA, fill = cluster)) +
geom_boxplot() +
theme(axis.text.x = element_text(angle = 45, hjust = 1))
确认cluster29是否为双细胞
scDblFinder 或 doubletScores 工具进行检测。检查 nCount_RNA 和 nFeature_RNA 的分布
若确定为双细胞或异常细胞,可将其从数据集中删除
# 删除cluster29
seu <- subset(seu, subset = !is.in.categorical("cluster", "29"))
重新运行UMAP或tSNE等降维分析
重新进行聚类和注释
如果你发现某个cluster在UMAP中位置偏移、表达量异常且细胞数少,它很可能是双细胞或异常细胞。在这种情况下,你可以安全地将它从数据集中删除,但需先进行充分验证。
如有需要,我可以帮助你进一步分析你的数据集或提供具体的代码示例。欢迎继续提问!