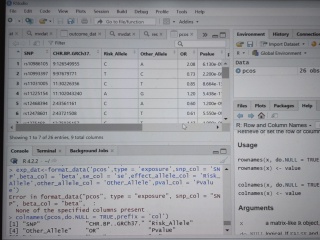
已经将snp的risk_allele和other_allele信息都读入R了,用colnames()检查列名好像也没错误,为什么想转换成twosample MR的格式,还是提示none of the specified columns present呢?

已经将snp的risk_allele和other_allele信息都读入R了,用colnames()检查列名好像也没错误,为什么想转换成twosample MR的格式,还是提示none of the specified columns present呢?
该回答引用GPTᴼᴾᴱᴺᴬᴵ
根据错误提示,您提供的数据中似乎缺少 risk_allele 列。请确保您的数据中包含此列,并且列名正确。如果您已经将其读入 R 中,请使用 colnames() 函数检查列名是否正确。
·
另外,如果您正在使用 format_data() 函数将数据转换为 MR 分析所需的格式,请确保您提供了正确的参数,例如 effect_allele_col 参数应该是 risk_allele。您可以使用 ?format_data 查看该函数的帮助文档,以确保您正确地使用了该函数。