- 经DPABI的ARWS预处理后的rsfMRI数据,在做FC和“Extract ROI Time courses”时总是报错,无论怎样定义ROI,提示“contained voxel = 0”。返回看预处理的数据,发现slice timing和realign的数据都没问题。而Normalize后的数据(在整个数据处理过程中,该步骤没有报错,生成的文件大小也有100M而非没有数据),用MRICorn打开,呈现一片空白。将realign后的数据overlay上去,提示“No overlap between overlay and background - these images do not appear coregistered”。具体的预处理流程如下图1,请问如何解决?
- 用的是DPARSF5.2版本的“DPARSF for monkey data”。有3个可能的影响因素:a,Normalize选择的是T1 image,在数据处理过程中,曾提示没有co*T1数据,用的是T1数据代替,见下图2。 b,Normalize一行的“Voxel size”是默认的{2 2 2},而实际是{1.5 1.5 1.5},是否有影响? c,预处理没有勾选“Bet”。勾选“Bet”后运行必然会报错,见下图3。不知原因为何?由于数据是同一只动物在同一次扫描中的多个session,故没有选“Bet”。
- 想看一次扫描内不同时间下(不同session)ROI随时间的变化,是否是选择“Extract ROI Time courses”?没有做个这个分析,不知“Extract ROI Time courses”得到的数据是什么样子,是每个session返回一个ROI的数值吗?多谢各位!
图1:
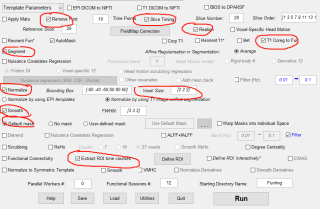
图2:
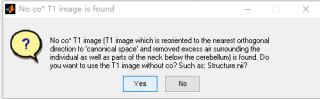
图3:

